Depto de Divulgación de Proyecto Primates Panamá/21 de abril de 2026
Las relaciones filogenéticas entre los monos ardilla (género Saimiri) han sido tradicionalmente difíciles de resolver. Mientras que las taxonomías basadas únicamente en la morfología proponían desde dos hasta doce taxones diferentes, los estudios moleculares más recientes llegaban a recuperar hasta 17 linajes distintos. El último listado taxonómico de referencia reconoce once formas: Saimiri boliviensis boliviensis, S. boliviensis peruviensis, S. vanzolinii, S. oerstedii oerstedii, S. oerstedii citrinellus, S. sciureus, S. collinsi, S. cassiquiarensis, S. albigena, S. macrodon y S. ustus. Para aclarar este panorama, un equipo liderado por Michelle P. Mercês reunió un conjunto de datos filogenómicos sin precedentes utilizando secuenciación de ADN asociada a sitios de restricción de doble digestión (ddRADseq), abarcando 57 muestras de toda la Amazonía y logrando construir la filogenia más robusta hasta la fecha para el género.
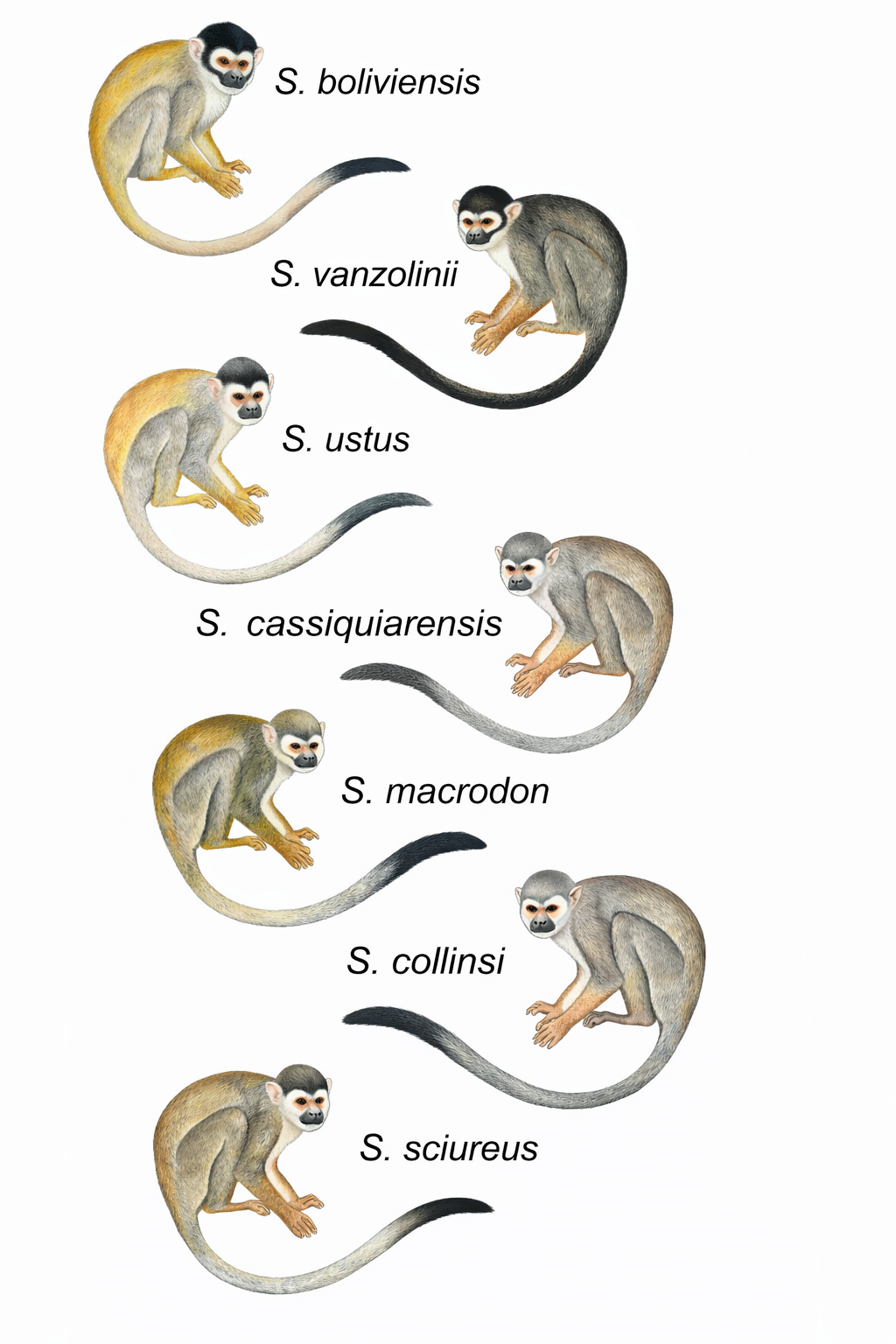 Todos los análisis filogenómicos (bayesianos, de máxima verosimilitud y de tiempos de divergencia) apoyaron de manera contundente la división de Saimiri en dos grandes clados, que coinciden perfectamente con los grupos morfológicos definidos por Hershkovitz: el grupo de arco gótico (Gothic) y el de arco romano (Roman). Dentro de ellos, se identificaron cinco linajes principales con un soporte máximo (probabilidad posterior de 1 y bootstrap de 100): (1) S. boliviensis + S. vanzolinii (grupo Romano); (2) S. ustus (el de orejas desnudas); (3) S. cassiquiarensis (noroeste amazónico); (4) S. macrodon (oeste amazónico); y (5) S. sciureus + S. collinsi (este amazónico). Esta topología resuelve las parafilias que mostraban los estudios mitocondriales previos y confirma la hipótesis morfológica, con la única excepción de una ligera parafilia en S. boliviensis que requerirá más muestreo.
Todos los análisis filogenómicos (bayesianos, de máxima verosimilitud y de tiempos de divergencia) apoyaron de manera contundente la división de Saimiri en dos grandes clados, que coinciden perfectamente con los grupos morfológicos definidos por Hershkovitz: el grupo de arco gótico (Gothic) y el de arco romano (Roman). Dentro de ellos, se identificaron cinco linajes principales con un soporte máximo (probabilidad posterior de 1 y bootstrap de 100): (1) S. boliviensis + S. vanzolinii (grupo Romano); (2) S. ustus (el de orejas desnudas); (3) S. cassiquiarensis (noroeste amazónico); (4) S. macrodon (oeste amazónico); y (5) S. sciureus + S. collinsi (este amazónico). Esta topología resuelve las parafilias que mostraban los estudios mitocondriales previos y confirma la hipótesis morfológica, con la única excepción de una ligera parafilia en S. boliviensis que requerirá más muestreo.
El árbol calibrado en el tiempo, construido con BEAST2, sitúa la diversificación de la corona de Saimiri a principios del Pleistoceno, hace aproximadamente 2,22 millones de años, con intervalos de confianza similares a los de estudios anteriores. La mayor parte de la especiación dentro de los grupos gótico y romano ocurrió durante el último millón de años, coincidiendo con los máximos glaciares y los cambios en la estructura y composición de los bosques amazónicos. Los análisis de estructura poblacional (Structure) no solo confirmaron la existencia de estos cinco linajes (con un K=6 que separa nítidamente cada uno), sino que también revelaron ancestría compartida entre algunos de ellos: por ejemplo, ciertos individuos de S. macrodon 1 presentan mezcla con el clado oriental, y parte de S. cassiquiarensis comparte ancestría con S. macrodon 2. Además, dentro del clado este, se detectaron tres agrupamientos geográficos bien diferenciados: la población de Faro/Juruti (a la que denominan S. collinsi ‘Faro y Juruti’), los S. sciureus de Amapá y los S. collinsi del sureste (Isla Marajó y sur de Pará).
Por último, los análisis de flujo génico con Dsuite encontraron múltiples evidencias de introgresión entre las especies del grupo gótico. Las señales más intensas (valores de f-branch > 0,05) se dieron entre S. collinsi ‘Faro/Juruti’ y S. sciureus (f = 0,2293), entre dos linajes de S. ustus (el ‘Xingu’ y el ‘ustus’ propiamente dicho, con f = 0,1712), y entre S. ustus y el ancestro del clado oriental. Estos resultados explican por qué los árboles mitocondriales (herederos solo por vía materna) mostraban parafilias extensas: la historia evolutiva de Saimiri incluye fenómenos reales de retención de linaje ancestral, introgresión y probablemente sesgo de dispersión por sexo, algo ya documentado en otras radiaciones rápidas de primates. En conjunto, este estudio no solo resuelve la filogenia del género, sino que también proporciona un marco para futuras revisiones taxonómicas, sugiriendo que algunas poblaciones (como la de Faro/Juruti o los dos linajes de S. macrodon) podrían merecer un estatus específico o subespecífico diferenciado. Queda pendiente incorporar taxones no muestreados como S. albigena y S. oerstedii, así como ampliar la cobertura de S. boliviensis peruviensis y de S. macrodon fuera de Brasil, para completar el rompecabezas evolutivo de estos carismáticos primates amazónicos.
Glosario de términos
-
ddRADseq (double digest restriction-site associated DNA sequencing)
Técnica de secuenciación genómica que utiliza dos enzimas de restricción para cortar el ADN en fragmentos específicos y luego secuenciar solo una parte representativa del genoma. Permite obtener miles de marcadores genéticos (SNPs) de manera económica, incluso en especies sin genoma de referencia completo. -
SNP (Single Nucleotide Polymorphism)
Variación en una sola posición del ADN (una letra del código genético) que es diferente entre individuos. Los SNPs son los marcadores moleculares más utilizados en estudios de filogenia y estructura poblacional por su abundancia en el genoma. -
Filogenia
Árbol evolutivo que representa las relaciones de parentesco entre especies o poblaciones. Cada ramificación indica un ancestro común y el orden en que se produjeron las divergencias. -
Clado
Grupo de organismos que incluye a un ancestro común y a todos sus descendientes. En un árbol filogenético, un clado es una rama completa (monofilética). -
Probabilidad posterior (Posterior probability, PP)
Medida de confianza en un nodo del árbol filogenético dentro de un análisis bayesiano. Valores cercanos a 1 indican un soporte muy alto (en este estudio, todos los nodos principales tuvieron PP = 1). -
Bootstrap
Técnica de remuestreo utilizada en análisis de máxima verosimilitud para evaluar la robustez de cada rama del árbol. Se expresa como porcentaje; valores cercanos a 100 % indican alta confianza. -
Introgresión
Transferencia de material genético de una especie a otra mediante hibridación y cruzamientos sucesivos (retrocruzamientos). No es lo mismo que hibridación ocasional: la introgresión deja una huella genética permanente en el genoma receptor. -
Flujo génico (gene flow)
Intercambio de genes entre poblaciones o especies diferentes. Puede ocurrir por migración de individuos fértiles. En el artículo, se detectó flujo génico incluso entre especies del grupo gótico. -
Structure
Programa informático que agrupa individuos en poblaciones genéticas (clusters) según la similitud de sus SNPs, sin información a priori sobre su taxonomía. Permite detectar ancestría compartida (individuos con mezcla de dos o más grupos). -
Dsuite
Herramienta bioinformática que calcula estadísticos como la D de Patterson y el f-branch para detectar señales de introgresión o flujo génico entre linajes, comparando el patrón de alelos compartidos con el esperado bajo un modelo de árbol sin mezcla. -
f-branch
Valor que cuantifica la proporción de alelos compartidos en exceso entre una población y una rama específica del árbol. Valores superiores a 0,05 se consideran evidencia sólida de flujo génico. -
Árbol calibrado en el tiempo (time‑calibrated tree)
Filogenia en la que la longitud de las ramas representa tiempo evolutivo (millones de años), no solo cantidad de cambios genéticos. Se obtiene usando fósiles o tasas de mutación conocidas como puntos de calibración. -
HPD (Highest Posterior Density)
Intervalo de credibilidad del 95 % para la edad estimada de un nodo en un árbol temporal. Indica el rango dentro del cual se encuentra la verdadera edad con una probabilidad del 95 %. -
Pleistoceno
Época geológica que abarca desde hace 2,58 millones hasta hace 11 700 años. Se caracterizó por repetidas glaciaciones. El estudio sitúa la diversificación de Saimiri a principios del Pleistoceno (~2,22 Ma). -
Grupo Gothic (arco gótico) y grupo Roman (arco romano)
Clasificación morfológica basada en la forma de la mancha blanca en forma de arco sobre los ojos de los monos ardilla. El arco gótico es anguloso (como un arco ojival) y el romano es redondeado. Esta división resultó ser genéticamente válida en el estudio. -
Parafilia / parafilético
Situación en la que un grupo taxonómico (por ejemplo, una especie) no incluye a todos los descendientes de un ancestro común. En el estudio, S. boliviensis apareció como parafilético (sus dos muestras no formaron un clado exclusivo), lo que sugiere que se necesita más muestreo. -
Ancestría compartida (shared ancestry)
En los análisis de Structure, indica que un individuo posee fracciones de su genoma provenientes de dos o más poblaciones/clusters diferentes. Es evidencia de mezcla genética. -
Linaje (lineage)
Línea evolutiva que comprende una secuencia de ancestros y descendientes. En el artículo se identifican cinco linajes principales dentro de Saimiri. -
Outgroup
Especie o grupo externo utilizado para “enraizar” el árbol filogenético. En este estudio se usó Sapajus robustus (un mono capuchino robusto), pariente cercano de los monos ardilla. -
BEAST2
Programa de análisis bayesiano que estima simultáneamente la filogenia y los tiempos de divergencia. Es uno de los estándares en filogenética molecular para árboles calibrados. -
iPyRAD
Pipeline bioinformático que ensambla y filtra datos de ddRADseq, llamando SNPs y generando matrices de presencia/ausencia de loci para análisis posteriores.

